打造“科学智能生态中枢”,驱动科学发现群体涌现,科学智能上下文协议(SCP)2.0发布 | AGI4S进行时
来源:上海人工智能实验室| 2026-02-28
当前,AI for Science正从辅助科研的“工具革命”1.0阶段,迈入以“革命的工具”驱动科学发现的2.0新时代。上海人工智能实验室(上海AI实验室)加速打造通专融合的人工智能,近期推出书生科学多模态大模型Intern-S1-Pro,通过底层架构创新推动通用能力与专业能力协同演进。与此同时,对书生科学发现平台Intern-Discovery进行了一系列更新,助力科学研究从团队单点探索迈向科学发现Scaling Law阶段:
调动多智能体协同的Intern·Agent升级为“推理驱动”的跨学科科学发现系统;支撑实验设备共享的科学智能上下文协议(Science Context Protocol,SCP)升级为“科学智能生态中枢”,并推动建设更开放的科学智能生态,助力科学发现“群体涌现”。
升级后的SCP 2.0将生物、化学、物理、材料科学、地球科学及数学与信息科学等六大学科领域的2200+工具API化,并通过Intern-Discovery的SCP广场为用户提供首批200余项“科学技能”(SCP Skill),让复杂实验流程轻松执行。
目前,北京大学、上海交通大学张江高等研究院、华大智造等合作伙伴已采用SCP开展科研,应用于蛋白质工程、新药研发早期筛选等干湿结合实验场景,助力提升实验自动化水平等,实现科研效率大幅提升。
SCP代码仓库与示例:https://github.com/InternScience/scp
SCP技术报告:https://arxiv.org/abs/2512.24189
SCP广场:https://scphub.intern-ai.org.cn/
Intern-Discovery链接:https://discovery.intern-ai.org.cn
SCP广场:共建科学智能生态,2200+工具一键使用
作为Intern-Discovery新设核心板块之一,SCP广场的主要功能为:集中发布和管理各类科研工具、模型、知识库、数据库与实验设备。目前,该广场已集成了涵盖生物、化学、物理、材料科学、地球科学及数学与信息科学六大领域的2200余项工具API,支持用户一键注册、快速使用。SCP Hub作为统一调用入口,提供智能工具发现、权限管控与调用管理等功能,降低了AI智能体构建和使用门槛。
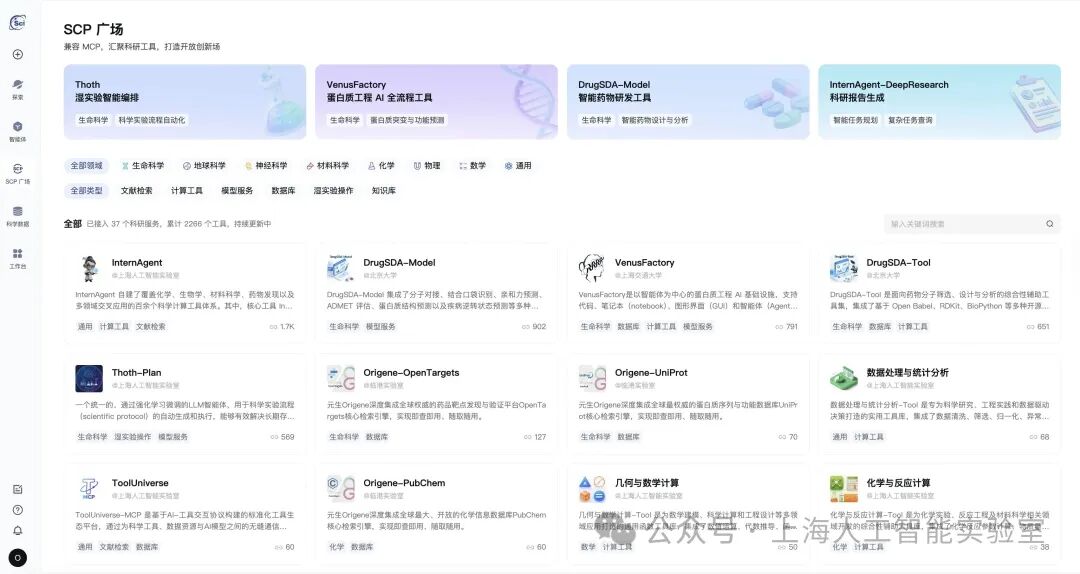
集成在Intern-Discovery上的SCP广场
2200余项科学工具均通过开放共建的生态模式汇聚而成。目前已有临港实验室、广州实验室、浙江大学、上海交通大学张江高等研究院等多家国内顶尖科研机构入驻,并将自研工具、数据库按照SCP协议标准完成封装和发布。
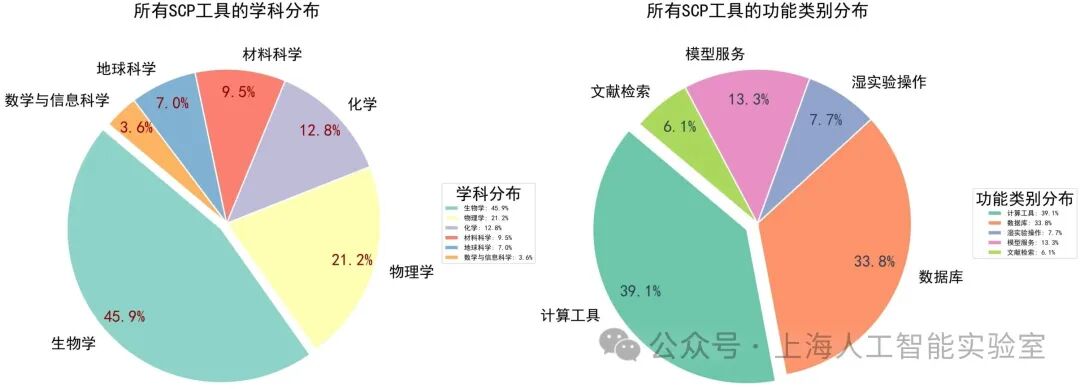
SCP科学工具在学科和功能类别上的数量分布
SCP Skill:200+Skill“触手可及”,让复杂实验流程轻松执行
通用领域的AI技能(Skill)多依赖于大模型自动编写代码,以此构建相对简单的工具;而科学领域的技能需要对科研活动中所涉及的复杂工具进行封装与直接调用,不仅要实现任务的高效完成、节省大模型的运算资源,更要提升科研流程的可执行性与可重复性。基于这一洞察,上海AI实验室提出“科学技能”(SCP Skill)概念,每一个Skill均为可独立调用、可自由组合的“科研指令”,背后串联多个数据库、计算模型及设备驱动工具API,构成可复用的标准化实验模版。科研团队基于SCP对科研全流程进行标准化拆解与封装,首批200余项SCP Skill已上线至Intern-Discovery。
这一创新对科研工作形成双重助力:对于科研人员,科学实验中无需再应对繁杂的工具手册与代码调试,可将精力聚焦于科学问题本身;对于AI智能体,Skill是可自由拼搭的“积木”,推动其从“工具使用者”向“实验设计师”转型。
⚪实例一:智能文献与知识检索,为科学假设找到证据链
在探索荧光蛋白酶亮度增强机制的研究中,上海交通大学张江高等研究院的洪亮教授团队面临海量文献与多源数据难以高效整合的困境。洪亮教授介绍,“SCP 2.0一站式的知识发现能力,为实验设计提供了高价值且可追溯的科学数据支撑。”例如,从文献中挖掘潜在突变位点并关联其功能机制,研究员通常需要数周甚至数月的手动检索和交叉验证。依托SCP广场集成的UniProt、PDB等权威数据库工具及多学科知识图谱,团队可一键发起跨库检索,系统能够从千万量级的科学文献中自动提取候选序列,同时在融合多学科知识的知识图谱中,精准定位与“荧光强度变化”相关的功能概念和作用通路,在数分钟内完成“文献挖掘-知识关联-结构建模-功能推断”的完整推理链条。
UserCase代码示例:https://github.com/InternScience/scp/blob/main/UserCases/ProteinMutation.ipynb
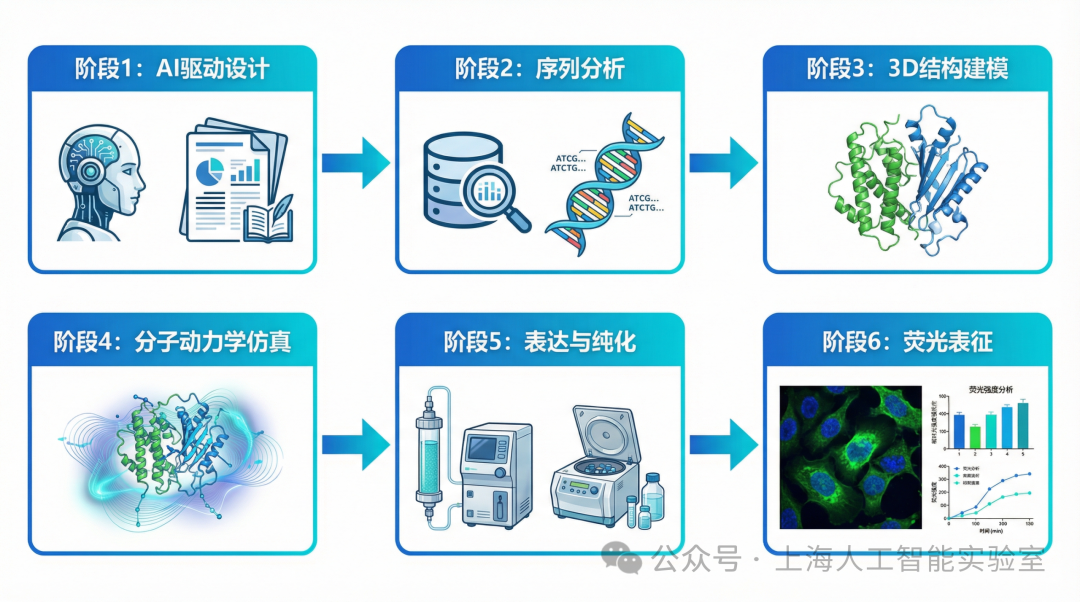
以蛋白质结构建模为例,SCP2.0覆盖从设计到分析再到建模的智能文献与知识检索驱动的流程
⚪实例二:专业工具全覆盖,药物筛选一站式完成
在新药研发的早期筛选阶段,通常涉及多个专业软件的串行使用,存在流程割裂、耗时费力等问题。北京大学谢正伟教授团队与上海AI实验室开展合作,“不仅将筛选效率提升数倍,更通过标准化流程保障了结果的一致性与可重复性。”依托SCP广场,谢正伟教授团队构建起了一套覆盖药物发现全流程的智能化工具链,实现一站式虚拟药物筛选:研究人员只需输入候选分子列表,系统便会自动调用QED评分、ADMET毒性预测模型完成初筛,随后自动抓取靶点蛋白结构并进行修复和口袋识别,最终启动分子对接。
UserCase代码示例:https://github.com/InternScience/scp/blob/main/UserCases/DrugMolScreening.ipynb
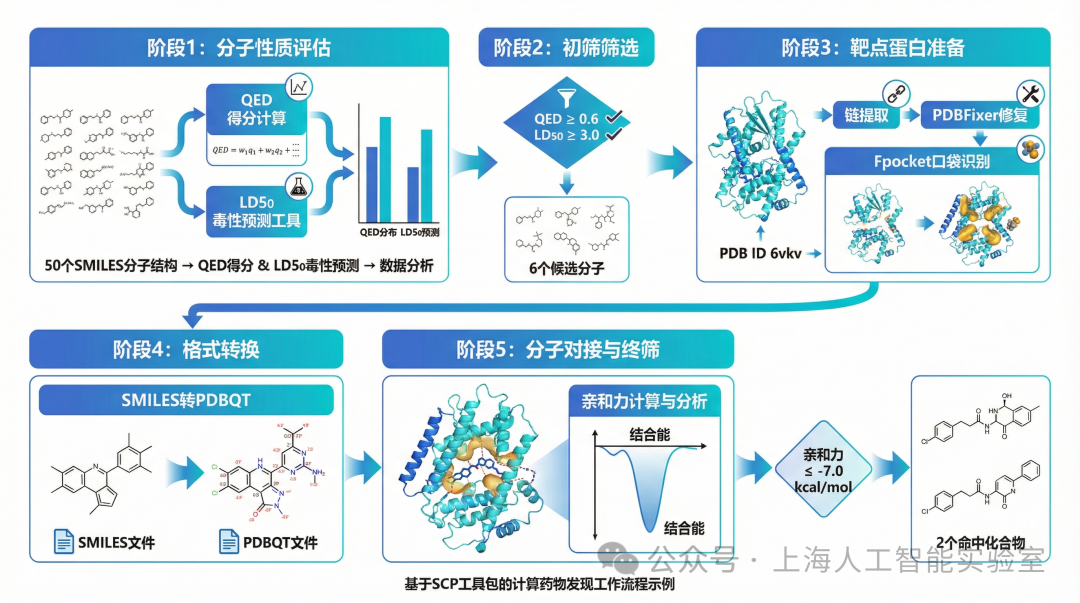
以新药研发为例,可以通过SCP 2.0完成早期筛选流程
⚪实例三:湿实验协议自动化生成,实现“干湿一体”闭环科研
SCP 2.0不仅实现了知识库与计算工具的连接,更构建起直达下游实验设备的完整闭环。通过集成Thoth协议理解服务器与ThothOP执行服务器,它可将PDF格式的实验方案直接转化为可执行的设备指令,大幅提升了华大智造实验自动化水平,该企业研发负责人坦言:“这为探索高通量、自动化的实验范式打开了全新的想象空间。以病原检测mNGS文库构建实验为例,传统模式需人工完成说明书解读、试剂配置、参数设置等繁琐操作,耗时且易出错;而依托SCP 2.0技术,上传PDF文档后系统可自动解析参数、生成指令并调度设备执行,同步回传分析数据,实现“AI设计-自动实验-数据反馈”闭环。
UserCase代码示例:https://github.com/InternScience/scp/blob/main/UserCases/Thoth.ipynb
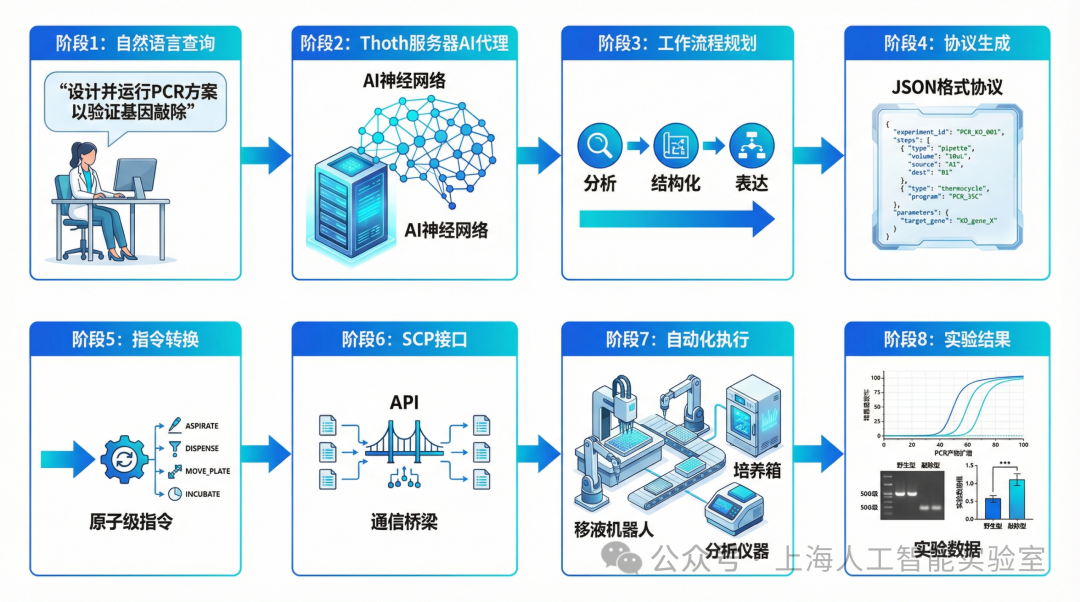
以病原检测mNGS文库构建为例,SCP 2.0实现了“AI设计-自动实验-数据反馈”的“干湿一体”实验闭环


